다양한 유전체 database를 바탕으로 항암 표적 유전자의 임상적 연관성 및 유전자의 기능적 분석 지원
서비스 내용
- GEO (Gene expression Omnibus), TCGA (The cancer genome atlas) 등의 Genomic data 분석을 통하여 항암 표적 유전자의 분자적인 특성 및 기능 분석
- Genomic data에서 항암 표적 유전자와 연관성이 있는 correlation 유전자를 선별하여 Ingenuity Pathway Analysis (IPA)를 활용한 유전자의 signaling pathway 분석
- 표적 유전자의 임상적 의의를 규명하기 위한 환자 생존율 분석 및 약물 반응 관련 연관성 분석
- cBioportal, Oncomine, KMPlot, GSEA 등의 Web browser를 활용한 표적 유전자의 유전자적 특성 분석 및 임상 샘플과의 연관성 분석
- 표적 유전자의 기능 규명을 위한 in vitro 실험 후 RNA-seq. data 분석 및 임상 샘플에서 연관성 분석

유전체 data를 활용한 표적 유전자의 발현 패턴 분석
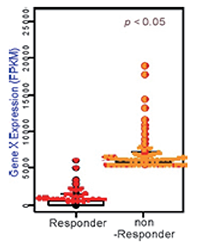
항암 표적 유전자의 약물 반응성 in silico 분석
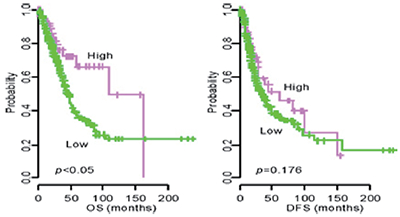
환자 유래 유전체 데이터를 이용한 표적 유전자와 생존율과의 연관성 분석
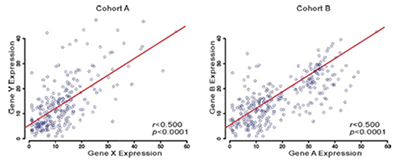
유전체 data를 활용한 특정 유전자 간의 연관성 규명





